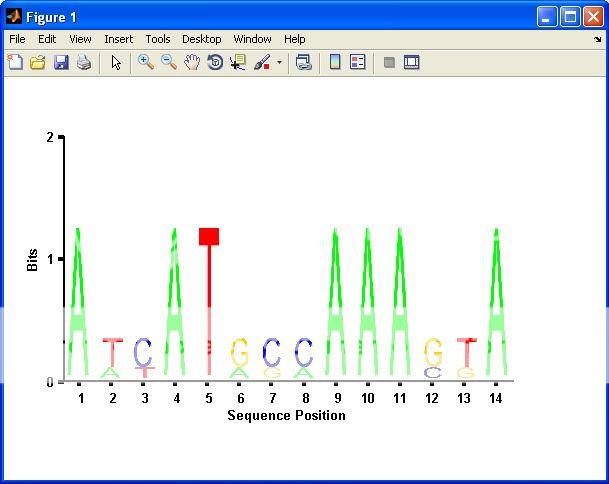
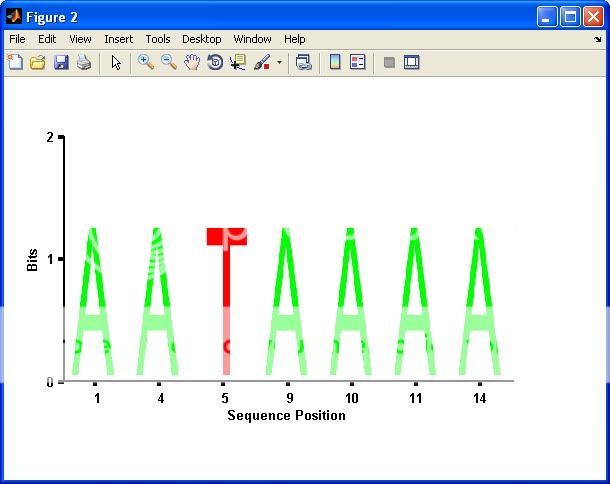
そこで、yukとgnoviceの両方のソリューションを使用して別のソリューションを作成しました。ソリューションを試してみると、出力を「サブプロット」として使用し、文字の色を任意に変更できるようにしたいと思いました。
yukは、文字が埋め込まれたプログラムで配置されたAxesオブジェクトを使用したため、コードを変更して任意のAxesオブジェクトにプロットするのは非常に面倒でした(不可能ではありませんが)。gnoviceのソリューションは、事前に作成されたファイルから文字を読み取るため、任意の配色または文字の選択に対して実行するようにコードを変更することは困難でした。したがって、私のソリューションでは、yukのソリューションの「文字生成」コードとgnoviceのソリューションの「画像スーパーインポーズ」メソッドを使用します。
かなりの量の引数の解析とチェックもあります。以下は私の組み合わせた解決策です...私は完全を期すためだけにそれを含めています、私は明らかに自分の賞金を獲得することはできません。私はコミュニティに賞を決定させ、制限時間の終わりに最高の評価を持っている人に賞金を与えます...同点の場合、私は最低の担当者(彼らはおそらくもっと「必要」です)。
function [npos, handle] = SeqLogoFig(SEQ, varargin)
% SeqLogoFig
% A function which wraps around the bioinformatics SeqLogo command
% and creates a figure which is actually a MATLAB figure. All
% agruements for SEQLOGO are passed along to the seqlogo calculation.
% It also supports extra arguements for plotting.
%
% [npos, handle] = SeqLogoFig(SEQ);
%
% SEQ A multialigned set of sequences that is acceptable
% to SEQLOGO.
% npos The positions that were actually plotted
% handle An axis handle to the object that was plotted.
%
% Extra Arguements:
%
% 'CUTOFF' A bit-cutoff to use for deciding which columns to
% plot. Any columns that have a MAX value which is
% greater than CUTOFF will be provided. Defaults to
% 1.25 for NT and 2.25 for AA.
%
% 'TOP-N' Plots only the top N columns as ranked by thier MAX
% bit conservation.
%
% 'AXES_HANDLE' An axis handle to plot the seqlogo into.
%
% 'INDS' A set of indices to to plot. This overrides any
% CUTOFF or TOP-N that were provided
%
%
%
%
%% Parse the input arguements
ALPHA = 'nt';
MAX_BITS = 2.5;
RES = [200 80];
CUTOFF = [];
TOPN = [];
rm_inds = [];
colors = [];
handle = [];
npos = [];
for i = 1:2:length(varargin)
if strcmpi(varargin{i}, 'alphabet')
ALPHA = varargin{i+1};
elseif strcmpi(varargin{i}, 'cutoff')
CUTOFF = varargin{i+1};
%we need to remove these so seqlogo doesn't get confused
rm_inds = [rm_inds i, i+1]; %#ok<*AGROW>
elseif strcmpi(varargin{i}, 'colors')
colors = varargin{i+1};
rm_inds = [rm_inds i, i+1];
elseif strcmpi(varargin{i}, 'axes_handle')
handle = varargin{i+1};
rm_inds = [rm_inds i, i+1];
elseif strcmpi(varargin{i}, 'top-n')
TOPN = varargin{i+1};
rm_inds = [rm_inds i, i+1];
elseif strcmpi(varargin{i}, 'inds')
npos = varargin{i+1};
rm_inds = [rm_inds i, i+1];
end
end
if ~isempty(rm_inds)
varargin(rm_inds) = [];
end
if isempty(colors)
colors = GetColors(ALPHA);
end
if strcmpi(ALPHA, 'nt')
MAX_BITS = 2.5;
elseif strcmpi(ALPHA, 'aa')
MAX_BITS = 4.5;
end
if isempty(CUTOFF)
CUTOFF = 0.5*MAX_BITS;
end
%% Calculate the actual seqlogo.
wm = seqlogo(SEQ, varargin{:}, 'displaylogo', false);
%% Generate the letters
letters = wm{1};
letter_wins = cell(size(letters));
[~, loc] = ismember(letters, colors(:,1));
loc(loc == 0) = size(colors,1);
clr = cell2mat(colors(loc, 2)); % corresponding colors
for t = 1:numel(letters)
hf = figure('position',[200 200 100 110],'color','w');
ha = axes('parent',hf, 'visible','off','position',[0 0 1 1]);
ht = text(50,55,letters(t),'color',clr(t,:),'units','pixels',...
'fontsize',100,'fontweight','norm',...
'vertical','mid','horizontal','center');
F = getframe(hf); % rasterize the letter
img = F.cdata;
m = any(img < 255,3); % convert to binary image
m(any(m,2),any(m,1))=1; % mask to cut white borders
letter_wins{t} = reshape(img(repmat(m,[1 1 3])),[sum(any(m,2)) sum(any(m,1)) 3]);
close(hf);
end
%% Use the letters to generate a figure
%create a "image" that will hold the final data
wmat = wm{2};
if isempty(npos)
if isempty(TOPN)
npos = find(any(wmat>CUTOFF,1));
else
[~, i] = sort(max(wmat,[],1), 'descend');
npos = sort(i(1:TOPN));
end
end
fig_data = 255*ones(RES(1), RES(2)*(length(npos)+1)+length(npos)*2,3);
bitscores = linspace(0, MAX_BITS, size(fig_data,1));
tick_pos = zeros(length(npos),1);
% place images of letters
for i=1:length(npos)
[wms idx] = sort(wmat(:,npos(i)), 'descend'); % largest on the top
bits = [flipud(cumsum(flipud(wms))); 0];
let_data = letter_wins(idx(wms>0));
for s=1:length(let_data)
start_pos = find(bitscores>=bits(s),1);
end_pos = find(bitscores<=bits(s+1),1, 'last');
if isempty(start_pos) || isempty(end_pos) || end_pos > start_pos
continue
end
img_win = imresize(let_data{s}, [start_pos-end_pos, RES(2)]);
fig_data(start_pos-1:-1:end_pos, (i*RES(2)-RES(2)*.5:i*RES(2)+RES(2)*.5-1)+2*i,:) = img_win;
end
tick_pos(i) = i*RES(2)+2*i;
end
if ~isempty(handle)
image(handle,[0 size(fig_data,2)], [0 MAX_BITS],fig_data./255)
else
handle = image([0 size(fig_data,2)], [0 MAX_BITS],fig_data./255);
end
set(gca, 'ydir', 'normal', 'xtick', tick_pos, ...
'userdata', tick_pos, 'xticklabel', npos);
xlabel('position')
ylabel('bits')
function colors = GetColors(alpha)
% get the standard colors for the sequence logo
if strcmpi(alpha, 'nt')
colors = cell(6,2);
colors(1,:) = {'A', [0 1 0]};
colors(2,:) = {'C', [0 0 1]};
colors(3,:) = {'G', [1 1 0]};
colors(4,:) = {'T', [1 0 0]};
colors(5,:) = {'U', [1 0 0]};
colors(6,:) = {'', [1 0 1]};
elseif strcmpi(alpha, 'aa')
colors = cell(21,2);
colors(1,:) = {'G', [0 1 0]};
colors(2,:) = {'S', [0 1 0]};
colors(3,:) = {'T', [0 1 0]};
colors(4,:) = {'Y', [0 1 0]};
colors(5,:) = {'C', [0 1 0]};
colors(6,:) = {'Q', [0 1 0]};
colors(7,:) = {'N', [0 1 0]};
colors(8,:) = {'A', [1 165/255 0]};
colors(9,:) = {'V', [1 165/255 0]};
colors(10,:) = {'L', [1 165/255 0]};
colors(11,:) = {'I', [1 165/255 0]};
colors(12,:) = {'P', [1 165/255 0]};
colors(13,:) = {'W', [1 165/255 0]};
colors(14,:) = {'F', [1 165/255 0]};
colors(15,:) = {'M', [1 165/255 0]};
colors(16,:) = {'D', [1 0 0]};
colors(17,:) = {'E', [1 0 0]};
colors(18,:) = {'K', [0 0 1]};
colors(19,:) = {'R', [0 0 1]};
colors(20,:) = {'H', [0 0 1]};
colors(21,:) = {'', [210/255 180/255 140/255]};
else
error('SeqLogoFigure:BADALPHA', ...
'An unknown alphabet was provided: %s', alpha)
end
これをMathworksFileExchangeに送信しました...承認されたら、リンクを投稿します。
私が抱えている唯一の厄介な問題は、文字の画像を作成するときに、小さな図のウィンドウが高速で表示されることです。誰かがそれを避けることができるトリックを知っているなら、私はそれを聞きたいです。
編集:Mathworksは私の提出されたファイルを承認しました...あなたはここのFileExchangeでそれをダウンロードすることができます:http://www.mathworks.com/matlabcentral/fileexchange/27124